近日,我所生物分离分析新材料与新技术研究组(1809组)叶明亮研究员团队开发了一款具有高灵敏度的N-糖肽质谱谱图解析新软件——Glyco-Decipher。该软件可实现在解析谱图的过程中不依赖糖库,利用不同糖肽的同一肽段骨架具有相似碎裂规律的特点,发展出基于“模式识别”的肽段序列鉴定新方法,实现谱图拓展,从而提高完整糖肽的鉴定灵敏度,并且可发现未知的糖链及糖链修饰。Glyco-Decipher为深度解析位点特异性糖型,揭示糖基化修饰的微观不均一性,以及研究糖生物学功能等提供了新工具。
蛋白质糖基化与疾病的发生发展密切相关,临床上使用的大多数肿瘤标志物是糖基化蛋白质。在组学层次上进行位点特异性糖型的分析对发现新型疾病标志物,提高基于蛋白质糖基化的精准医学研究水平等具有重要作用。
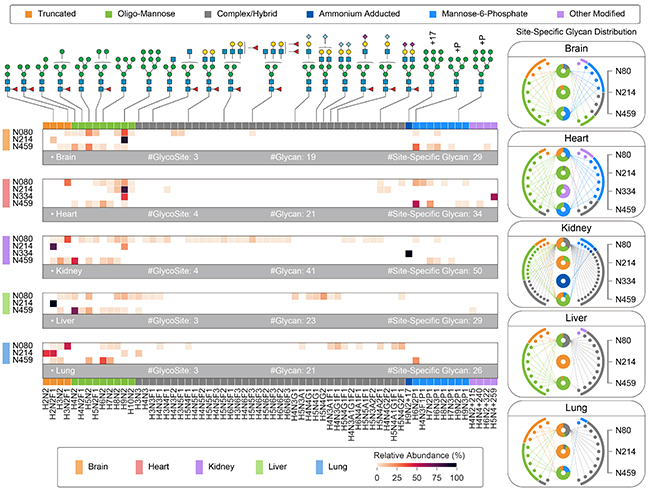
N-糖肽质谱谱图高度复杂,谱图解析率低,且常规N-糖肽解析软件依赖糖库,无法实现未知糖链及修饰糖的鉴定。为解决上述问题,本工作开发了非糖库依赖的肽段序列鉴定方法,实现了未知糖链肽段及其上可能带有的修饰基团的鉴定。为解决N-糖肽质谱谱图解析率低的问题,团队系统研究了糖肽的碎裂规律,发现糖链的种类、组成、母离子价态等对肽段骨架的碎裂模式没有显著的影响,建立了肽段序列相同的完整糖肽谱图之间的联系,发展了基于“模式识别”的肽段序列鉴定策略,实现了完整糖肽的谱图拓展,在原有基础上将完整糖肽的解析率提升了31%。
本工作还以蛋白Prosaposin为例,展示了蛋白Prosaposin在老鼠的五个不同的组织中糖基化差异,进一步揭示了该蛋白上各个位点特异性糖型的丰度分布,展示了Glyco-Decipher在蛋白糖基化分析领域的应用潜力。通过对同一个N-糖肽质谱数据进行对比分析,发现Glyco-Decipher的谱图解析效率比其它软件提升了34-179%。该软件具有友好的用户界面和较好的定量比较功能,学术界可以免费使用(软件可从github下载)。
叶明亮团队长期致力于位点特异性糖型分析方法的发展,包括糖肽的富集方法和谱图的解析方法:在O-GlcNAc糖肽的富集方面发展了酶促标记结合化学氧化法(Anal. Chem.,2021)、可逆酶促化学标记法(Angew. Chem. Int. Edit.,2022)等方法;在O-GalNac糖肽的富集方面发展了酶解辅助的亲水作用色谱法(Anal. Chem.,2017)、酶化学方法(Anal. Chem.,2018)、Ti-IMAC富集方法(Anal. Chem.,2021)等;在N糖肽的富集方面发展了适合大样本分析的自动化富集方法(Anal. Chem.,2021);在O-GalNac糖肽的谱图解析方面,发展了O-search检索策略(Anal. Chem., 2019),有效地减小了检索空间,提高了鉴定灵敏度。最近,上述检索策略被集成于一款具有自主知识产权的谱图检索软件——MS-Decipher(Bioinformatics,2022)中。
相关研究成果以“Glyco-Decipher Enables Glycan Database-independent Peptide Matching and in-depth Characterization of Site-specific N-glycosylation”为题,于近日发表在《自然-通讯》(Nature Communications)上。该工作的共同第一作者是1809组博士研究生方正和秦洪强研究员。上述工作得到国家重点研发计划、国家自然科学基金、我所创新基金等项目的支持。(文/图 方正)